Резюме. Проведён анализ нуклеотидной последовательности гипервариабельного сегмента 1 (ГВС1) и 16 маркеров кодирующего региона митохондриальной ДНК в этнической группе карачаевцев. По результатам проведённой работы в популяции карачаевцев была обнаружено 21 гаплогруппа митохондриальной ДНК (мтДНК). В изученной популяции преобладает западноевразийский компонент, составляющий 91,1%.
Восточноевразийский компонент представлен четырьмя гаплогруппами, составляющими в общей сложности 8,9% изученной выборки, из которых 6,5% приходится на гаплогруппу О, которая с высокими частотами встречается в Северо-Западной и Центральной Азии. По результатам анализа главных компонент (РСА) показано удаление карачаевцев от лингвистически родственных балкарцев и сближение с группой абхазо-адыгских народов. Уровень генетического разнообразия (Н) в изученной популяции составил 0,9688. анализ показал сближение популяции карачаевцев с народами, населяющими территорию Западного Кавказа.
Ключевые слова: карачаевцы, митохондриальная ДНК, гаплогруппа, Северный Кавказ
Актуальность. По данным Российской академии наук в настоящее время в мире насчитывается 39 живых тюркских языков [1]. Всероссийская перепись 2010 года зафиксировала 28 тюркских народов на территории России общей численностью 12 млн. человек [2]. Широкому распространению представителей этой языковой группы по Евразийскому материку способствовали их многовековые миграции. И хотя значение древних тюрок в истории человечества было огромным [3], история их современных потомков остаётся одной из наиболее дискуссионных в современной науке. Карачаевцев, населяющих горные и предгорные районы центральной части Северного Кавказа, не обошла стороной данная проблема. Вопрос о появлении карачаевцев в горах Центрального Кавказа требует особого подхода в том числе потому, что по имеющимся данным представители тюркской лингвистической группы имеют общие сегменты ДНК с популяциями южной Сибири и Монголии [4]. При этом по результатам множества работ выявлена более тесная связь тюркских народов с географически близкими соседями, нежели с родственными лингвистически популяциями [5-6].
В ряде работ уже были изучены популяции Северного Кавказа с использованием различных систем маркеров [5, 7-11]. Однако постоянная эволюция методов изучения с использованием большего филогенетического разрешения, а также новые изучаемые выборки способствуют лучшему изучению интересующей проблематики.
Материал и методы исследования. Для проведения работы в 2014 году была собрана уникальная выборка биоматериала из 123 представителей карачаевского этноса. Забор крови проходил в Карачаево-Черкесской Республике в местах компактного проживания данного этноса (а. Верхняя Мара, а. Верхняя Теберда, с. Дружба, с. Знаменка, а. Каменомост, г. Карачаевск, с. Первомайское, а. Сары-Тюз, а. Терезе, с. Учкекен и г. Черкесск). Участниками научного исследования было подписано информированное согласие, а также заполнена анкета с указыванием предков до третьего поколения включительно.
Нами проанализирована нуклеотидная последовательность гипервариабельного сегмента 1 (ГВС1), а также 16 маркеров кодирующего региона мтДНК: C5178A, T10034C, G13708A, A10550G, T7028C, T14766C, T1391C, C12633A, A14233G, A13104G, A14139G, T4646C, G4580A,G1719A, G13368A, G8251A.
Выделение ДНК из цельной крови проводилось стандартным фенолхлороформным методом [12].
Секвенирование мтДНК проводилось на автоматическом секвенаторе Applied Biosistems (ABI) 3730 XL DNA Analyzer. Анализирование результатов секвенирования проводилось при помощи программы ChromasPro 2.4.1. Гаплогруппы и гаплотипы определялись в результате анализа сайтов рестрикции кодирующего региона митохондриальной ДНК (мтДНК) с использованием ПЦР с последующим ПДРФ анализом или методом секвенирования.
Оценка степени генетической дифференциации между популяциями проводилась с помощью показателей матрицы попарных дистанций Слаткина (Fst) [13] в программе Arlequin 3.11 [14]. Факторный анализ проводился с применением метода главных компонент с использованием статистического пакета R. Также были определены индекс генетического разнообразия (Н), индекс абсолютного числа выявленных гаплотипов (k), число полиморфных сайтов (S), среднее число попарных нуклеотидных различий (Pi), а также индексы тестов на нейтральность Таджимы (D) и Фу (FS).
Полученные результаты и их обсуждение. Данные, полученные в результате проведённого исследования, показывают значительное преобладание в популяции карачаевцев западноевразийских гаплогрупп (91,1%) (Таблица 1). С наибольшей частотой среди них представлены гаплогруппы Н и U1, которые в сумме составляют 32,52% митохондриального пула карачаевцев. Восточноевразийский компонент состоит из четырёх гаплогрупп, среди которых выделяется встречающаяся в Северо-Западной и Центральной Азии [15] гаплогруппа О. Сравнительно высокая частота данной гаплогруппы у карачаевцев связана с эффектом основателя.

Одной из важнейших биологических характеристик популяций является генетическое разнообразие. Так, в результате статистических расчетов уровень генетического разнообразия (Н) в популяции карачаевцев оказался довольно высоким и составил 0,9688. Об экспоненциальном росте численности популяции говорит достоверно высокое отрицательное значение Fs-теста Фу (-25.00860), проведенного в программе Arlequin 3.11. При помощи теста Таджимы мы оценили отклонение от модели нейтрально эволюционирующей, а также демографически стабильной популяции. Тест нейтральности мтДНК Таджимы оказался достоверным для карачаевцев (-1.43922) и свидетельствует о прохождении популяцией через «бутылочное горлышко» с последующим периодом экспоненциального роста (Таблица 2).
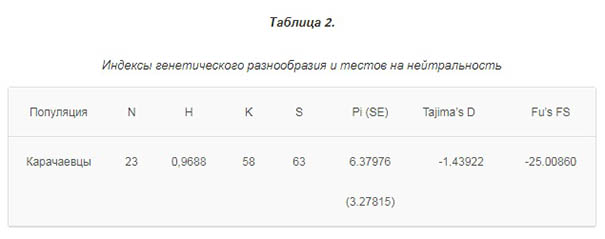
Примечание. N — размер выборки; Н — генетическое разнообразие; К — число выявленных гаплотипов; S — число полиморфных сайтов; Pi — среднее число нуклеотидных различий при попарных сравнениях и стандартная ошибка ^Е); Tajima‘s D — тест на нейтральность Таджимы (Р < 0.05) и Fu‘s FS — тест на нейтральность Фу (Р < 0.02).
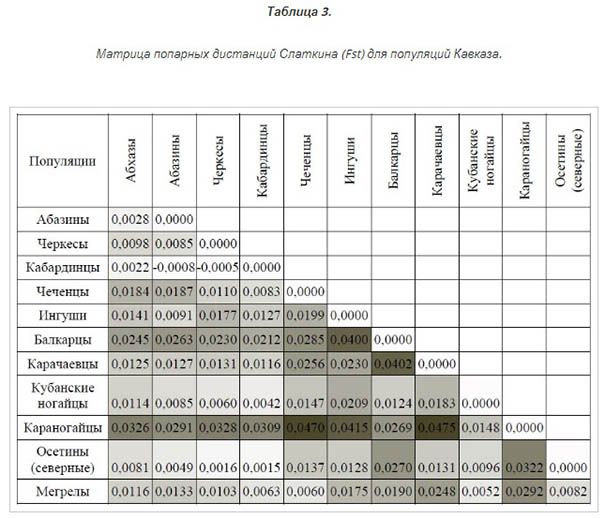
Для оценки генетической близости между различными популяциями Кавказа был проведён анализ Fst (Таблица 3). По данному анализу можно сделать вывод о генетической близости карачаевцев с популяциями, относящимися к адыго-абхазской языковой группе. Интересно, что наибольшее удаление наблюдается между карачаевцами и ближайшими их географическими соседями — балкарцами, относящимся также к тюркской языковой группе.
Генетическое взаимоотношение между популяциями Кавказа показано в пространстве двух главных компонент. По результатам анализа наблюдается удаление карачаевцев по второй главной компоненте от лингвистически родственных балкарцев и сближение их с народами Западного Кавказа.
Выводы. По результатам анализа гаплогрупп митохондриальной ДНК выявлено преобладание западноевразийских гаплогрупп в популяции карачаевцев (91,1%). Восточноевразийский компонент представлен по большей части гаплогруппой О. Сравнительно высокое содержание этой гаплогруппы связано с эффектом основателя, о чём говорят однообразные мотивы у большинства её носителей (16 223-16362). Данные статистических анализов показывают высокий уровень генетического разнообразия (Н) в изученной популяции (0,9688), а также экспоненциальный рост численности популяции, произошедший, по всей видимости, после прохождения ею через «бутылочное горлышко». В результате проведённых анализов Fst и PCA показана близость изученной популяции карачаевцев с популяциями Западного Кавказа.
Исследование поддержано РФФИ (грант №17-44-020748 р_а) и программой поддержки биоресурсных коллекций ФАНО.
ФГБОУ ВО «Башкирский государственный университет», кафедра генетики и фундаментальной медицины
ФГБОУ ВО «Башкирский государственный университет», кафедра генетики и фундаментальной медицины
Учреждение Российской академии наук Институт биохимии и генетики Уфимского научного центра РАН
ФГБОУ ВО «Башкирский государственный университет», кафедра генетики и фундаментальной медицины
Эстонский биоцентр, Тартуский университет, Тарту, Эстония
Эстонский биоцентр, Тартуский университет, Тарту, Эстония,
Эстонская академия наук, Таллинн, Эстония
ФГБОУ ВО «Башкирский государственный университет», кафедра генетики и фундаментальной медицины,
Учреждение Российской академии наук Институт биохимии и генетики Уфимского научного центра РАН
1. Языки мира: Тюркские языки. — Москва: Российская академия наук, 1996 г. — 543 с.
3. Гумилёв Л.Н. Древние тюрки / Л.Н. Гумилёв. — Москва: Изд-во Айрис-Пресс, 2016. — 560 с.
4. The Genetic Legacy of the Expansion of Turkic-Speaking Nomads across Eurasia / В. Yunusbayev [et al.] // PLos.Genet. — 2015. — Vol. 11, № 4.
5. The Caucasus as an asymmetric semipermeable barrier to ancient human migrations / B. Yunusbayev [et al.] // Mol. Biol. Evol. — 2012. — Vol. 29, №1. — P. 359-365.
6. Autosomal and uniparental portraits of the native populations of Sakha (Yakutia): implications for the peopling of Northeast Eurasia / S. Fedorova [et al.] // BMC evolutionary biology. — 2013. — Vol. 13:127.
7. Genetics and population history of Caucasus populations / K. Bulayeva [et al.] // Hum. Biol.- 2003.- V. 75№ 6.- P. 837-853.
8. Origin and Expansion of Haplogroup H, the Dominant Human Mitochondrial DNA Lineage in West Eurasia: the Near Eastern and Caucasian Perspective / U. Roostalu [et al.] // Mol. Biol. Evol.- 2007.- V. 24. №. 2.- P. 436-448.
9. Кутуев, И.А. Генетическая структура и молекулярная филогеография народов Евразии / И.А. Кутуев, Э. К Хуснутдинова // Уфа: Гилем, 2011. — 239 c.
10. Генофонд этнических групп Кавказа по данным комплексного исследования Y-хромосомы, митохондриальной ДНК и полногеномного анализа / Э. К. Хуснутдинова [и др.] // Генетика. — 2012. — Т. 48, № 6. — С. 750-761.
11. Генетическая характеристика балкарцев и карачаевцев по данным об изменчивости Y— хромосомы / М. Джаубермезов [и др.] // Генетика. — 2017. — Т. 53, № 10. — С. 1224-1231.
12. The isolation of high molecular weight eukaryotic DNA / C. Mathew // Methods Mol. Biol. — 1985. — Vol. 2. — P. 31-34.
13. Measure of population subdivision based on microsatelite allele frequencies / M. Slatkin // Genetics. — 1995. — Vol. 139. — P. 457-462.
14. Schneider S. Arlequin version 2.000: a software for population genetics data analysis / S. Schneider, D. Roessli and L. Excoffier // Geneva: University of Geneva, Genetics and Biochemistry laboratory, 2000.
15. Admixture, migrations, and dispersals in Central Asia: evidence from maternal DNA lineages / D. Comas [et al.] // European Journal of Human Genetics. — 2004. — Vol. 12. — P. 495-504.












 100
100
 65
65







